Guide complet sur l'identification et la caractérisation des protéines

L'identification et la caractérisation des protéines constituent l'un des aspects les plus importants de l'expression et de la fabrication de protéines recombinantes pour les produits biologiques. Elles font appel à une grande variété d'outils et de techniques analytiques en raison de la grande complexité des protéines elles-mêmes, qui sont composées de 21 acides aminés disposés selon un nombre quasi infini de combinaisons, puis repliées en structures tridimensionnelles.
Comprendre la structure d'une protéine est essentiel pour comprendre sa fonction, et la création de thérapies biologiques, notamment d'anticorps, de protéines recombinantes, de vaccins et d'autres molécules, dépend d'une caractérisation claire et précise.
Méthodes d'identification des protéines
- Spectrométrie de masse (MS) – Les protéines entières sont d'abord ionisées, puis introduites dans un analyseur de masse, ou identifiées au niveau peptidique. Le spectromètre identifie la structure des protéines par empreinte de masse ou spectrométrie de masse en tandem. Les masses peptidiques sont comparées à des bases de données en ligne afin d'établir les correspondances protéiques les plus proches.
- Dégradation d'Edman – Purifie les protéines en éliminant un résidu à la fois à partir de l'extrémité amino d'un peptide, à l'aide d'isothiocyanate de phényle. Le processus n'endommage pas la protéine et sépare un résidu à la fois, mais n'est pas aussi utile pour les protéines plus grosses.
- Empreinte peptidique – Cette méthode à haut débit fait appel à des endoprotéases qui clivent les protéines inconnues en peptides plus petits. La masse de ces peptides peut être mesurée à l'aide d'un spectromètre de masse, et les listes de « pics peptidiques » obtenues sont comparées à des bases de données protéiques.
- Recherche dans des bases de données et outils bioinformatiques – Les données issues de la spectrométrie de masse et de l'empreinte génétique sont comparées à l'aide de programmes informatiques et de bases de données afin de trouver la correspondance la plus proche avec votre échantillon.
- Immunoessais – Identifient les protéines grâce à leurs interactions avec des anticorps spécifiques. Ces tests comprennent les tests ELISA (dosages immuno-enzymatiques), le western blotting (séparation des protéines par poids moléculaire, transfert par électrophorèse sur une membrane et sondage avec des anticorps) et l'immunoprécipitation (précipitation d'un antigène protéique hors de la solution à l'aide d'un anticorps qui se lie spécifiquement à cette protéine).
- Chromatographie d'exclusion stérique (SEC) – À l'aide de billes de dimensions spécifiques placées dans une colonne, ces méthodes séparent les protéines en fonction de leur taille. Lorsque les échantillons pénètrent dans la colonne, les différentes molécules ont des vitesses d'élution différentes.
- Chromatographie d'affinité – Cette technique utilise également une colonne et des billes de cellulose. Un substrat (ou parfois une coenzyme) est lié de manière covalente aux billes situées au sommet de la colonne. Les protéines qui possèdent un site de liaison pour le substrat immobilisé se lieront, tandis que toutes les autres protéines seront éluées.
Techniques de caractérisation des protéines
La caractérisation des protéines permet d'élucider la séquence primaire, la structure d'ordre supérieur, les modifications post-traductionnelles, les interactions et les activités biologiques des protéines. La caractérisation des protéines fait appel à un large éventail d'outils et de techniques analytiques. Il n'existe pas de technologie universelle permettant de déterminer la composition chimique, la structure et la fonction de grosses molécules présentant différents états d'agrégation, charges, tailles et configurations tridimensionnelles. Cependant, la caractérisation des protéines présentes dans vos échantillons, en particulier celles susceptibles d'être utilisées à des fins thérapeutiques, est essentielle pour déterminer la sécurité, l'efficacité et la pureté de vos traitements à base de protéines.
Équipement d'analyse des protéines
L'analyse des protéines fait appel à des outils qui détectent, purifient et identifient les protéines, puis commencent à caractériser leur structure et leur fonction. Les équipements peuvent inclure des méthodes traditionnelles telles que l'électrophorèse, qui sépare les protéines en fonction de leur taille et de leur charge, le western blot, qui marque les cibles avec des anticorps, et la spectrométrie de masse, qui mesure les rapports masse/charge. Les méthodes plus modernes incluent la diffusion dynamique de la lumière (DLS).
- La séparation des protéines (électrophorèse) consiste à placerles protéines dans un gel et àobserver leur mobilité en présence d'un champ électrique. Les protéines peuvent être séparées en fonction de leur solubilité, de leur taille, de leur charge et de leur liaison. La méthode la plus courante est la SDS-PAGE (abréviation de « sodium dodecyl sulfate polyacrylamide gel electrophoresis », ou électrophorèse sur gel de polyacrylamide au dodécylsulfate de sodium), qui sépare les protéines en fonction de leur poids moléculaire.
- Le Western blotting identifieles protéines extraites des cellules, les sépare par taille, les transfère sur un support solide (le blot) et utilise des anticorps primaires et secondaires pour cibler les protéines, permettant ainsi leur identification sur la base d'associations biologiques.
- La diffusion de la lumière est une approche plus moderne, plus sensible avec les molécules de plus grande taille. Par exemple, la DLS permet de détecter avec précision de petites quantités d'agrégats polypeptidiques dans les préparations.La gamme Aura Systems mesureavec précision la distribution granulométrique, sur la base de l'imagerie membranaire en arrière-plan (BMI) et de la microscopie membranaire à fluorescence (FMM). Ces instruments fournissent des informations précieuses sur la distribution granulométrique des particules dans un échantillon, aidant ainsi les chercheurs et les fabricants à comprendre les caractéristiques de leurs produits.
Instruments de formulation biologique
Lors de la fabrication de molécules thérapeutiques, il est important de disposer des instruments adéquats pour surveiller la conformation des protéines, prédire leur stabilité thermique et mesurer la formation d'agrégats.
Calorimétrie différentielle à balayage (DSC) caractérise la stabilité thermique des protéines en mesurant l'enthalpie (ΔH) et la température (Tm) des transitions structurelles induites thermiquement des molécules. La DLS peut analyser la mobilité et la charge des particules (potentiel zêta) à l'aide de la technique de diffusion électrophorétique de la lumière (ELS), ainsi que le poids moléculaire des particules en solution à l'aide de la diffusion statique de la lumière (SLS). D'autres systèmes, tels que Aura PTx System, utiliser IMC avec deux canaux de FMM pour détecter et identifier les particules invisibles à l'œil nu qui peuvent former des agrégats et menacer la stabilité des produits biologiques. De plus, la FMM permet également de caractériser les excipients des formulations, tels que le polysorbate.
Outils de caractérisation des protéines
Chromatographie:la chromatographie liquide haute performance (CLHP), la chromatographie d'exclusion stérique (SEC), la chromatographie d'échange d'ions (IEC) et la chromatographie d'affinité séparent les protéines en fonction de leur taille, de leur charge, de leur hydrophobicité ou d'interactions spécifiques, ce qui permet d'analyser la pureté et de séparer les isoformes ou les variants protéiques.
Électrophorèse:la SDS-PAGE, la focalisation isoélectrique (IEF) et l'électrophorèse capillaire (CE) séparent les protéines en fonction de leur taille, de leur charge ou de leur point isoélectrique, facilitant ainsi l'analyse de la pureté, la composition des sous-unités et les modifications post-traductionnelles.
MS:La chromatographie liquide couplée à la spectrométrie de masse (LC-MS) et la spectrométrie de masse à désorption/ionisation laser assistée par matrice (MALDI-MS) identifient et quantifient les protéines, les peptides et les modifications post-traductionnelles, élucidant ainsi la séquence primaire, les variations structurelles et les interactions.
Spectroscopie:la spectroscopie ultraviolet-visible (UV-Vis), la spectroscopie de fluorescence, le dichroïsme circulaire (CD) et la spectroscopie par résonance magnétique nucléaire (RMN) permettent l'analyse structurelle des protéines ainsi que l'analyse du repliement, des changements conformationnels et de la liaison des ligands.
The Aura Systems family (en particulier le système Aura PTx pour les protéines) utilise une combinaison de BMI, une méthode de microscopie, et de microscopie à membrane fluorescente, qui utilise des colorants fluorescents ou des anticorps pour une caractérisation plus rapide et plus fiable, le tout sur un seul instrument. Grâce aux systèmes Aura, les chercheurs peuvent comprendre la stabilité et la pureté des protéines produites.

Essais de caractérisation des protéines
Essais biophysiques :la DLS et la DSC caractérisent la taille, la forme, la stabilité et les interactions des protéines avec des ligands ou d'autres molécules.
Les tests immunologiques: ELISA, Western blotting, immunoprécipitation et cytométrie en flux permettent de détecter et de quantifier les protéines, les épitopes ou les interactions protéine-protéine spécifiques, facilitant ainsi les tests immunologiques, la détection des biomarqueurs et les études sur les interactions protéine-protéine.
Formulation protéique
Le processus d'assemblage de la structure primaire des protéines (acides aminés), suivi des structures secondaire et tertiaire (tridimensionnelle) pour obtenir les produits protéiques pharmaceutiques finaux, nécessite des étapes qui garantissent la stabilité, l'intégrité structurelle et la fonction. La protéine doit être stabilisée afin de tolérer les processus de fabrication et de rester stable et active pendant le transport, le stockage et l'administration. Le développement de la formulation vise à garantir la stabilité, l'efficacité, la sécurité et la fabricabilité des produits biopharmaceutiques en sélectionnant des excipients, des tampons, un pH et des formes posologiques appropriés.
Les facteurs qui influencent la stabilité et l'efficacité comprennent la formation d'agrégats, qui a un impact sur la structure des protéines (et donc sur leur fonction). Il est important de distinguer les ingrédients pharmaceutiques actifs (IPA) agrégés des autres types de particules afin de comprendre la cause profonde de l'instabilité. The Aura PTx System’s Le système d'imagerie des agrégats et des particules à 96 puits permet de mesurer rapidement la taille, de compter et de caractériser les particules, puis de les identifier comme étant des protéines, des non-protéines, des excipients ou d'autres types de molécules. Ce système est beaucoup plus efficace et précis que les systèmes traditionnels à cellule d'écoulement utilisés pour distinguer la taille et le nombre des protéines.
Analyse de l'agrégation des protéines
Les agrégats présents dans les échantillons de protéines sont généralement des segments de chaînes polypeptidiques brisées qui « accompagnent » la fabrication des thérapies protéiques. Ils peuvent toutefois réduire considérablement la stabilité de la protéine cible et diminuer l'efficacité d'un agent thérapeutique. De plus, l'exposition à l'air, à des solides, à la lumière ou à des variations de température (qui font souvent partie du processus de développement pharmaceutique) peut produire des particules protéiques.
Pour réussir, les thérapies protéiques nécessitent des mesures de la qualité des produits à la fin de la phase de découverte et au début du développement, qui permettent de détecter, de compter et de caractériser les excipients des formulations, garantissant ainsi la stabilité des protéines. Cependant, les méthodes traditionnelles nécessitent des heures de tri d'images et des volumes relativement importants, ainsi que l'adoption de bibliothèques d'apprentissage automatique complexes, et négligent souvent les agrégats d'échantillons clés et les composés dégradés. Aura PTx System, grâce à la combinaison de l'IMC et de deux canaux FMM, fournit rapidement le nombre, la taille et la morphologie, et différencie les agrégats cellulaires, protéiques ou extrinsèques.
Caractérisation du poids moléculaire
Les techniques permettant de caractériser les protéines en fonction de leur poids moléculaire comprennent la SDS-PAGE, la MALDI-TOF MS et la SEC ou SEC-MALS. La SDS-PAGE est la technique la plus courante et sépare les protéines en fonction de leur poids moléculaire (et non en fonction de leur charge ou de leur repliement). Elle est souvent utilisée en biochimie, en médecine légale, en génétique et en biologie moléculaire. La MALDI-TOF est une forme de spectrométrie de masse qui détermine le rapport masse/charge, qui détermine les masses et la composition élémentaire des protéines. Une fois le MALDI développé, cette technique est devenue populaire pour étudier les protéines. La SEC, également connue sous le nom de filtration sur gel ou HPLC, est une technique puissante pour l'analyse des agrégats et des fragments dans la recherche, le développement et la fabrication de protéines biothérapeutiques, telles que l'insuline et les anticorps monoclonaux.
Analyse de pureté par HPLC
Comme mentionné ci-dessus, la HPLC est utilisée pour les études de pureté des protéines. Elle permet une séparation hautement sélective des échantillons. La HPLC sépare les molécules en fonction de leur taille par filtration à travers un gel. Le gel est constitué de billes contenant des pores d'une distribution de taille, d'une charge et/ou d'une affinité spécifiques. La séparation se produit lorsque des molécules de tailles, de charges ou d'affinités différentes sont incluses ou exclues des pores de la matrice. Les analytes plus gros s'éluent en premier, tandis que les molécules plus petites interagissent davantage avec la phase stationnaire et s'éluent plus tard.
Analyse des variants de charge protéique
Les protéines biothérapeutiques de grande taille peuvent subir des modifications enzymatiques post-traductionnelles au cours de leur fabrication, telles que la glycosylation et la troncature de la lysine. De plus, des modifications chimiques peuvent se produire pendant la purification et le stockage. C'est pourquoi la FDA et d'autres organismes de réglementation exigent que ces protéines soient soumises à une analyse des variants de charge. Cette analyse était traditionnellement réalisée à l'aide d'une chromatographie d'échange d'ions avec des gradients de sel, tandis que les techniques plus récentes s'appuient sur des gradients de pH plutôt que sur le sel. La focalisation isoélectrique par CE a également été utilisée comme méthode globale rapide, mais elle nécessite encore des temps d'exécution plus longs et est sujette à l'erreur humaine. Elle nécessite souvent un échantillon très pur, car elle ne permet pas de traiter correctement les échantillons contaminés ou hétérogènes.
Agrégation et analyse du contenu des fragments
Les agrégats et les fragments sont des impuretés courantes dans les produits biopharmaceutiques qui ont un impact sur l'efficacité, la sécurité et la stabilité des produits. La SEC peut être couplée à la spectrométrie de masse à ionisation par électrospray pour la caractérisation des variantes de taille des anticorps monoclonaux thérapeutiques (mAbs). La spectrométrie de masse quadripolaire à temps de vol (Q-TOF) peut également être optimisée pour une plus grande sensibilité. De plus, l'ultracentrifugation analytique peut aider à séparer les fragments.
Identification et quantification des résidus protéiques des cellules hôtes
Les protéines de la cellule hôte sont des impuretés produites par l'organisme hôte pendant la fabrication des produits biothérapeutiques. La purification élimine généralement la plupart de ces résidus du produit final, mais les protéines résiduelles qui restent dans le traitement par anticorps fabriqué, même à de faibles concentrations, peuvent être immunogènes. La FDA et d'autres organismes de réglementation exigent aujourd'hui que les produits biothérapeutiques finaux ne contiennent pratiquement aucune impureté protéique. Les techniques de spectrométrie de masse sont utiles pour l'identification et la quantification des protéines de la cellule hôte présentes dans les produits thérapeutiques recombinants, et constituent une amélioration par rapport à la méthode ELISA et à d'autres méthodes d'analyse. Les techniques d'analyse par microscopie BMI et FMM du système Aura PTx peuvent également être très efficaces pour détecter les protéines et les agrégats.
Couverture de séquence/cartographie peptidique
Il est essentiel de déterminer la séquence exacte et précise de votre protéine thérapeutique pour réussir sa caractérisation. Cette méthode consiste à digérer les protéines jusqu'à leurs peptides fondamentaux et garantit une séquence complète de la molécule biothérapeutique. Les techniques de couverture de séquence et de cartographie peptidique comprennent la HPLC et la HPLC couplée à la MS. Les techniques MS peuvent fournir des données très précises et sélectives, en particulier avec des biomolécules très complexes comme les mAbs.
Confirmation des séquences N-terminale et C-terminale
L'analyse de la séquence amino (N-terminale) identifie l'ordre des acides aminés de votre protéine, en commençant par l'extrémité N-terminale. Les séquences N-terminales ont un impact significatif sur la demi-vie, la localisation subcellulaire et les modifications post-traductionnelles des protéines. De même, l'analyse de la séquence C-terminale (terminal acide) identifie l'ordre des acides aminés à l'extrémité C-terminale de la protéine. Cela peut fournir des informations sur le repliement des protéines, la structure secondaire et la disposition des domaines fonctionnels. Les deux principales méthodes utilisées pour confirmer cette séquence sont la spectrométrie de masse (MS) et la dégradation d'Edman.
Analyse des modifications post-traductionnelles
Les modifications post-traductionnelles (PTM) sont des variantes introduites dans les protéines après leur expression. Des études épigénétiques ont montré que les PTM peuvent être inoffensives ou modifier considérablement la fonction des protéines. Il est donc nécessaire de détecter les effets des PTM dans tout produit biothérapeutique. Les PTM courantes peuvent aller des plus simples aux plus complexes et comprennent la phosphorylation, la glycosylation, l'ubiquitination, la nitrosylation, la méthylation, l'acétylation, la lipidation et la protéolyse. Elles sont le plus souvent enzymatiques (causées par l'action d'enzymes). Les techniques d'identification et d'analyse des PTM peuvent varier en fonction du type de PTM et comprennent la SDS-PAGE, le Western blot, l'immunoprécipitation de chromatine (ChIP) et d'autres techniques.
Analyse des liaisons disulfure
Les liaisons disulfure sont des liaisons covalentes entre les atomes de soufre présents sur les résidus de l'acide aminé cystéine. Elles constituent le seul lien covalent entre les polypeptides et stabilisent la structure des protéines. Les agents réducteurs tels que le chlorhydrate de tris (2-carboxyéthyl) phosphine (TCEP), le bêta-mercaptoéthanol (BME) et le dithiothréitol (DTT) peuvent perturber les liaisons disulfure et donc la stabilité des protéines. L'analyse des liaisons disulfure est généralement effectuée par MS et HPLC.
Analyse des modifications glycosylées
La glycosylation des protéines est une modification post-traductionnelle importante qui peut modifier le repliement, la conformation, la distribution, la stabilité et l'activité des protéines. La glycosylation implique l'ajout de divers sucres aux protéines, qui contrôlent ensuite la fixation des cellules à la matrice extracellulaire et les interactions protéine-ligand dans la cellule. Les glycoprotéines sont détectées, purifiées et analysées, dans l'ordre, par coloration et visualisation des glycanes, réticulation des glycanes à l'agarose ou à la résine magnétique pour le marquage ou la purification, ou analyse protéomique par MS.
Analyse des sites de glycosylation et des glycoformes
La glycosylation varie en fonction de l'endroit où la molécule de sucre se lie dans la cellule, ainsi que de la structure et du site de liaison chimique de la molécule de sucre. Ces oligosaccharides peuvent influencer les interactions protéine-protéine en permettant ou en empêchant les protéines de se lier à des domaines d'interaction apparentés. Étant hydrophiles, ils peuvent également modifier la solubilité des protéines. Les techniques d'analyse comprennent la coloration des glycanes, l'enrichissement et l'analyse à l'aide de lectines, ainsi que la spectrométrie de masse.
Analyse de l'acide sialique
L'acide sialique est le sucre le plus répandu à la surface des cellules mammifères. Il est essentiel à l'adhésion cellulaire et à la modulation immunitaire, et se lie aux sélectines et aux lectines. L'analyse de l'acide sialique et des monosaccharides est requise par les directives ICH Q6B pour la production biopharmaceutique. En général, l'acide sialique est quantifié par marquage fluorescent et analyse par HPLC avec détection fluorescente.
Présentation générale : Technologie de caractérisation des protéines
Les protéines sont sans doute les molécules les plus complexes des cellules et tissus vivants, et leur utilisation dans les produits biopharmaceutiques nécessite l'intégration de diverses technologies pour une analyse complète afin de garantir leur sécurité et leur efficacité.
Caractérisation MS
Comme décrit précédemment, la SM est un outil précieux pour caractériser et analyser les protéines ainsi que les fragments, les agrégats et les PTM qui peuvent avoir un impact sur le développement et la stabilité des protéines. Les techniques de SM sont utilisées pour déterminer la structure, la fonction, le repliement et les interactions, identifier les protéines à partir de leur masse de fragments peptidiques et compter avec précision les protéines dans un échantillon. Le développement de la protéomique MS quantitative et à haut débit au cours des 20 dernières années a élargi le champ d'application de la MS.
Caractérisation par spectrométrie CD
La CD mesure l'absorption différentielle de la lumière polarisée circulairement à gauche et à droite par des composés optiquement actifs à différentes longueurs d'onde. La lumière incidente sur l'échantillon alterne entre la lumière LCP et la lumière RCP. Lorsque la lumière incidente change de direction de polarisation, l'absorption change et l'absorbance molaire différenciée peut être calculée. La CD permet d'étudier les changements de structure secondaire et prépare le terrain pour une analyse conformationnelle des protéines. La CD peut également être utilisée pour examiner la stabilité des protéines/acides nucléiques (pliage, dépliage et repliage) en présence de pH, de dénaturants, de température et d'autres facteurs.
FMM/SIMI/BMI
Constituant la base de l'analyse des protéines et des fragments de protéines réalisée à l'aide des systèmes Aura, Aura PTx System est le premier et le seul système qui combine IMC) avec deux FMM) canaux permettant de fournir rapidement le nombre, la taille, l'identifiant, l'imagerie et la morphologie avec des agrégats cellulaires et protéiques différenciés, des excipients tels que le polysorbate dégradé et/ou la caractérisation des particules extrinsèques.
DLS
Le DLS est utilisé pour mesurer des particules de 0,2 nm à 10 µm. Ces instruments fonctionnent selon le principe du mouvement brownien, selon lequel les particules plus légères se déplacent plus rapidement que les particules plus lourdes (et donc plus grosses). Un laser illumine les particules et la lumière diffusée est analysée. Les fluctuations d'intensité déterminent la distribution granulométrique d'un échantillon.
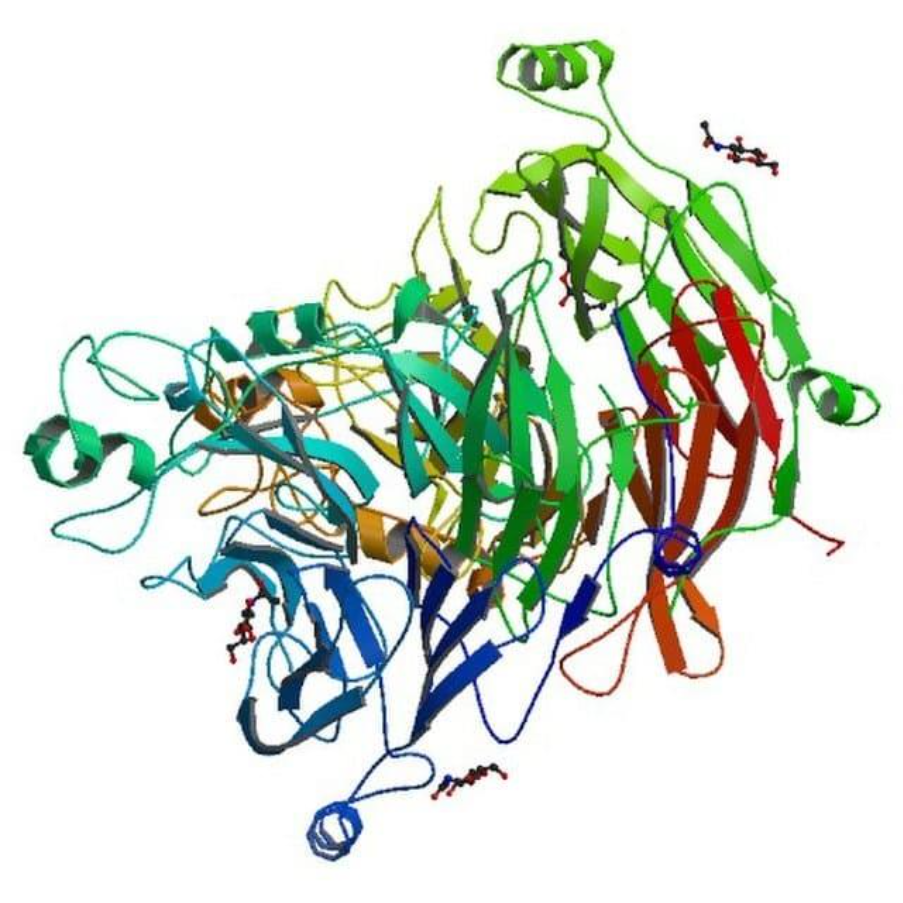
Caractérisation par cristallographie aux rayons X
La cristallographie aux rayons X repose sur la capture d'images radiographiques lorsque les rayons X traversent une forme cristallisée d'une molécule cible (dans ce cas, une protéine). Il s'agit d'une méthode précise pour déterminer la structure tridimensionnelle d'une protéine. Pour utiliser cette technique, le cristallographe obtient des cristaux de protéines, enregistre le diagramme de diffraction formé par les rayons X qui traversent les cristaux, puis interprète les données à l'aide d'un logiciel informatique. Le résultat est un modèle atomique d'une protéine.
Caractérisation par spectroscopie par résonance magnétique nucléaire
La résonance magnétique nucléaire (RMN) se produit lorsque les noyaux dans un champ magnétique immobile sont perturbés par un champ magnétique oscillant ; les noyaux génèrent un signal électromagnétique dont la fréquence dépend du champ magnétique appliqué. Avec la cristallographie aux rayons X et la microscopie électronique cryogénique, la RMN est l'une des trois techniques utilisées pour élucider la structure des protéines. Contrairement à l'imagerie par résonance magnétique nucléaire, la RMN des protéines utilise des algorithmes pour créer des modèles tridimensionnels de l'échantillon étudié. La RMN des protéines est réalisée sur des échantillons soigneusement purifiés.
Caractérisation par cryo-microscopie électronique
Autre technique permettant de déterminer la structure d'une protéine, la cryo-microscopie électronique est une technologie émergente et prometteuse qui permet d'obtenir des structures de protéines membranaires à haute résolution, ce qui est impossible avec d'autres techniques telles que la RMN ou la cristallographie aux rayons X. La cryo-EM comprend plusieurs applications telles que l'analyse de particules individuelles (SPA), la cryo-tomographie électronique (cryoET) et la microdiffraction électronique (MicroED). Elle a révolutionné la biologie structurale, la recherche sur les maladies infectieuses et la découverte de médicaments.

Faire progresser la caractérisation des protéines
En raison de la nature complexe (sans parler de l'importance) des protéines, il est nécessaire de développer des approches intégratives combinant plusieurs techniques pour une analyse complète et une caractérisation des protéines. Les tendances futures en matière de caractérisation semblent s'orienter vers des débits plus élevés et une meilleure résolution au niveau atomique, ainsi que vers la capacité à déterminer rapidement et de manière fiable les non-protéines et les fragments et agrégats protéiques, en particulier à mesure que de plus en plus de biothérapies à base de protéines sont développées et commercialisées.
Références
Sujets populaires
ACQUITY QDa (17) bioanalyse (12) produits biologiques (17) biopharmacie (50) produits biopharmaceutiques (59) biothérapies (24) étude de cas (20) chromatographie (14) intégrité des données (23) analyse alimentaire (12) HPLC (15) informatique (12) LC-MS (27) chromatographie en phase liquide (LC) (25) détection de masse (16) spectrométrie de masse (MS) (61) développement de méthodes (13) analyse des particules (21)